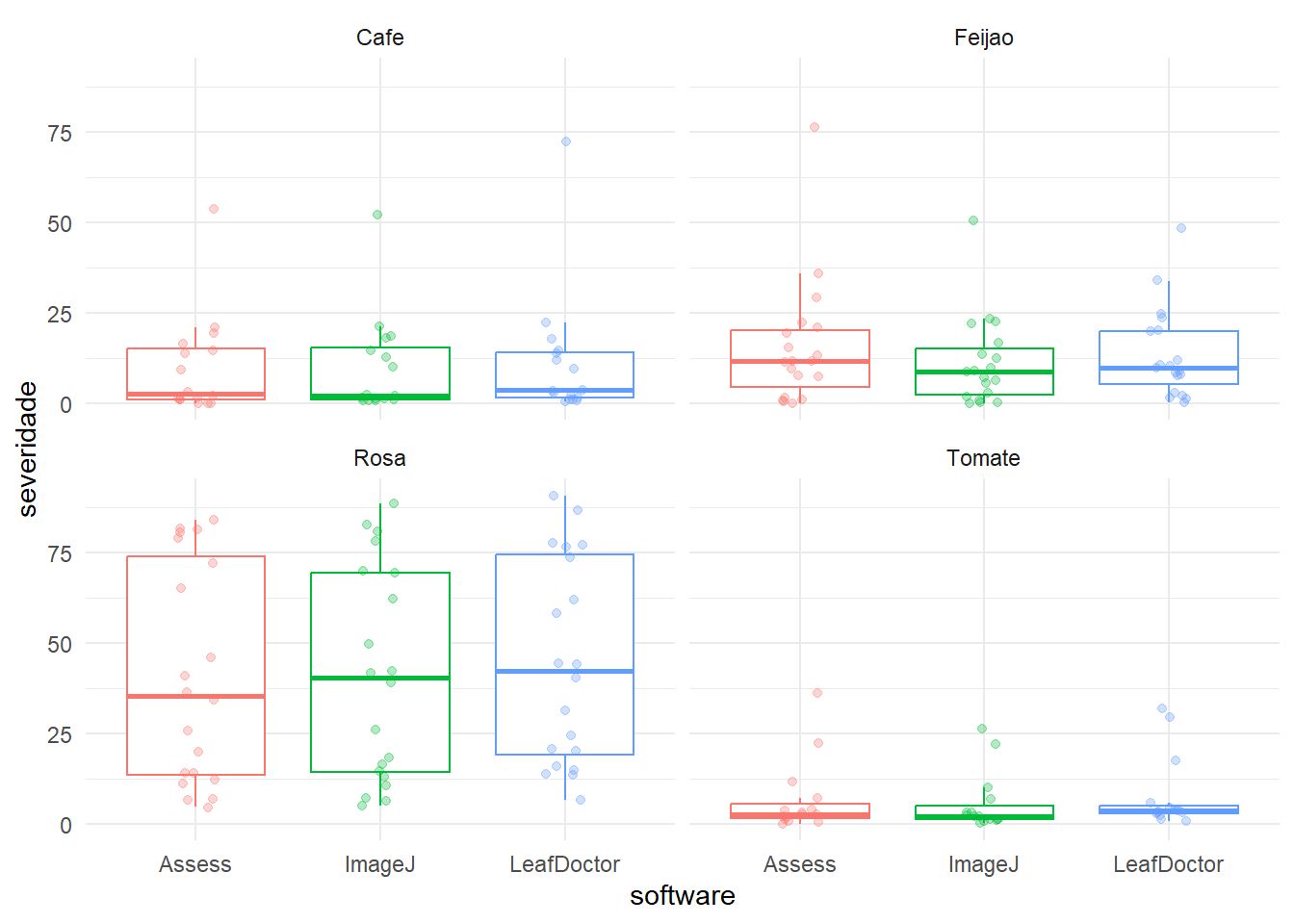
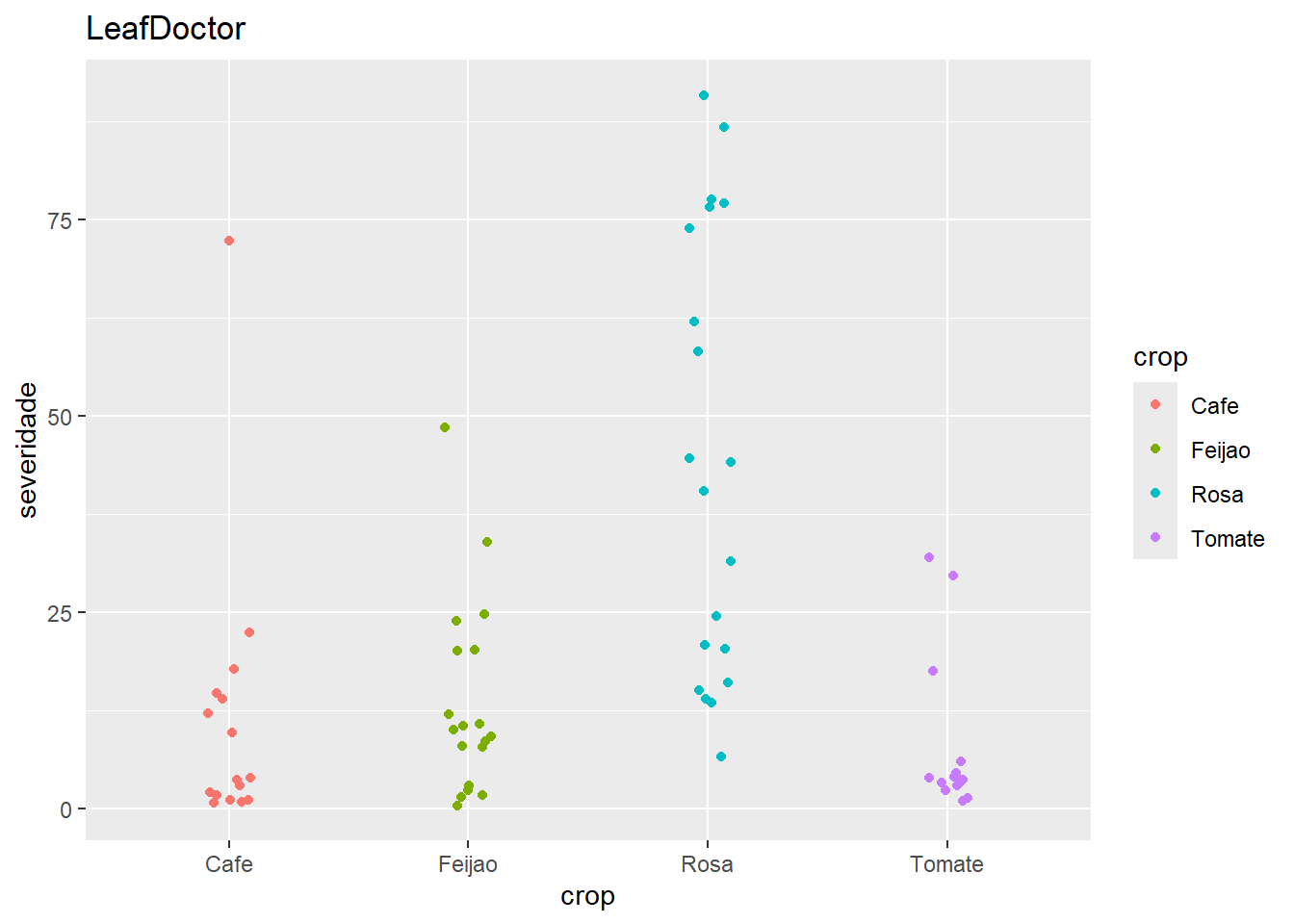
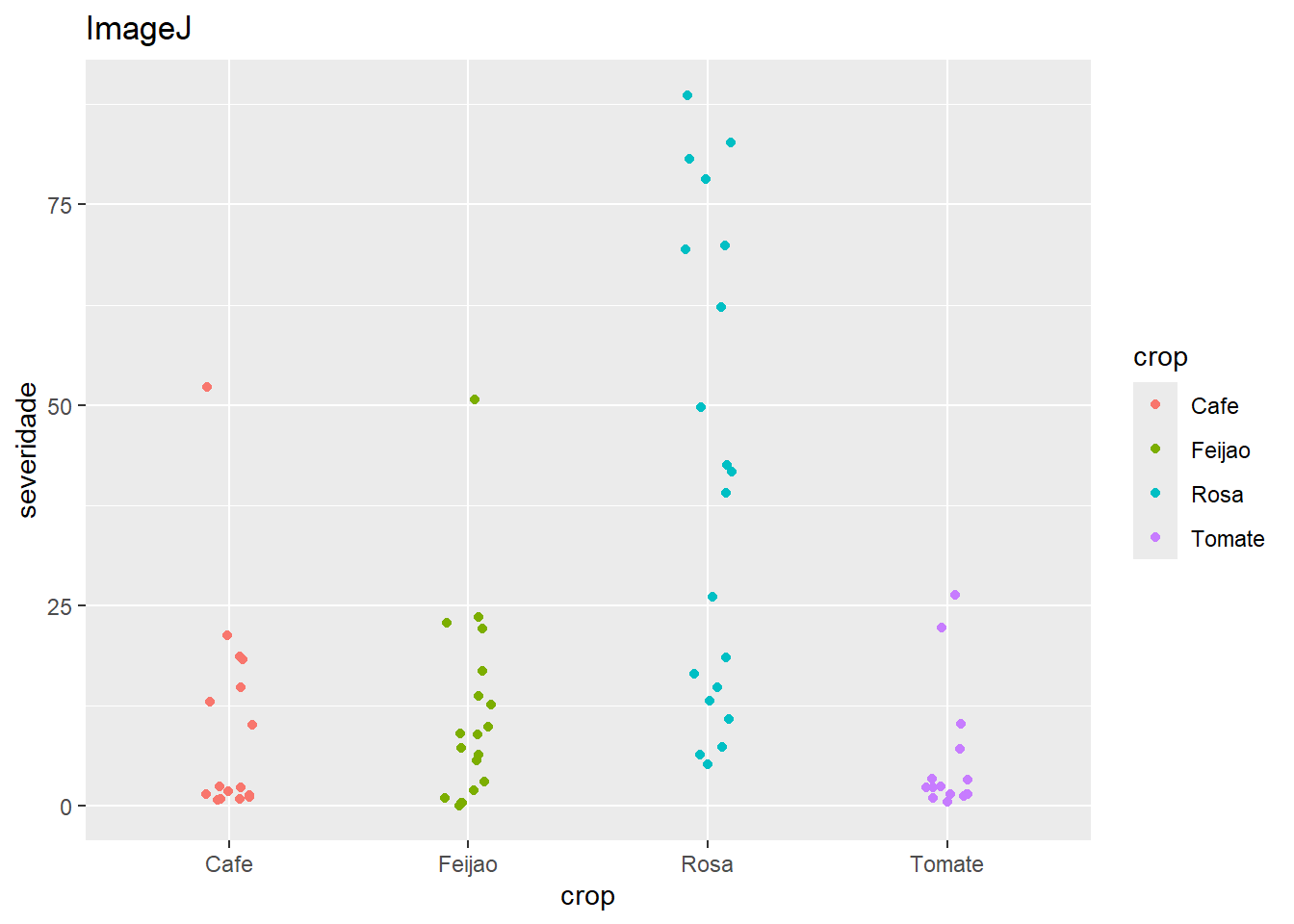
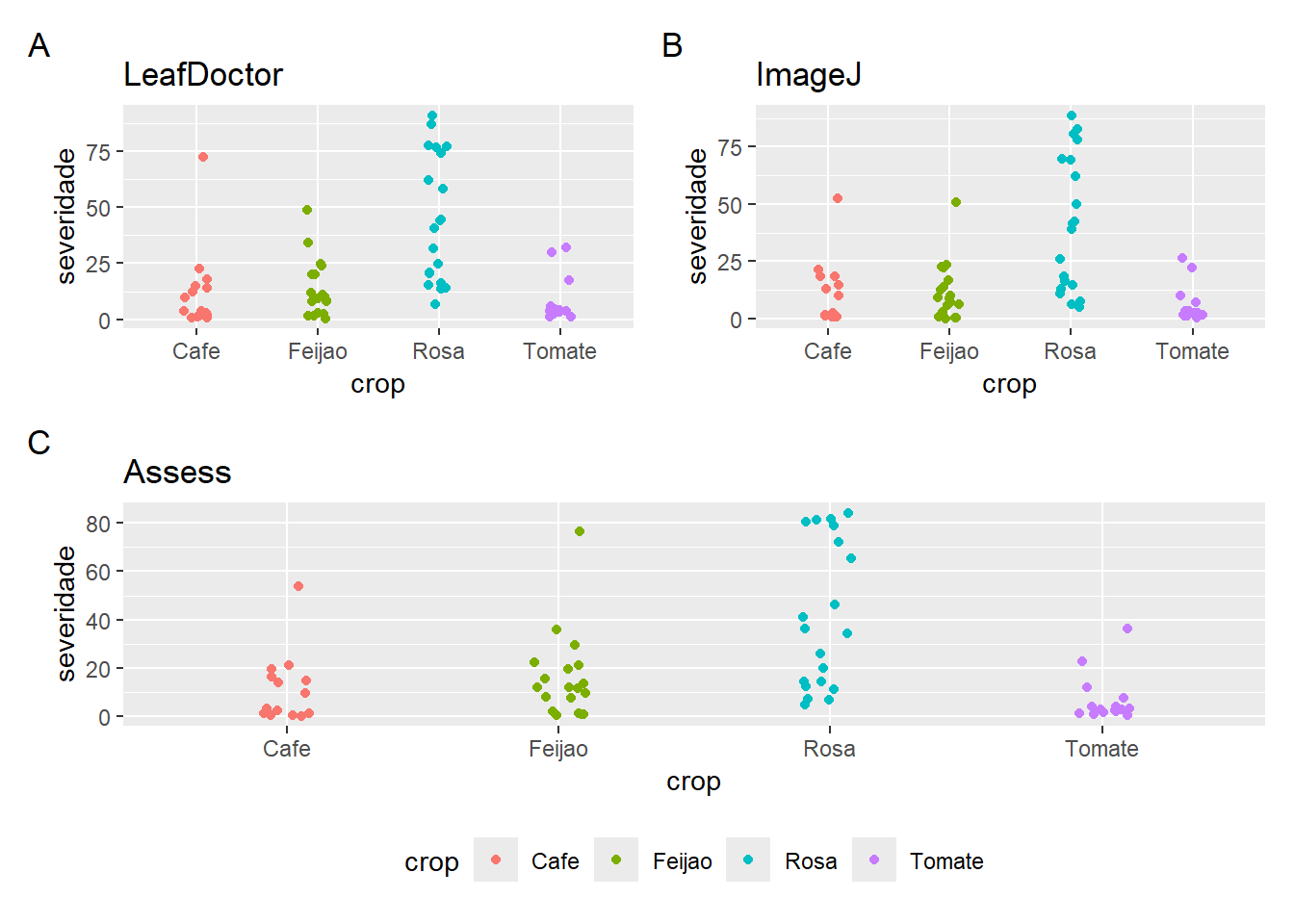
# Carrega o pacote readxl, usado para ler arquivos .xls e .xlsx
library(readxl)Warning: pacote 'readxl' foi compilado no R versão 4.4.3# Importa a aba "coffee rust" do arquivo Excel local
meudado <- read_excel(
"dados_diversos.xlsx",
sheet = "coffee rust"
)
# Exibe o objeto importado
meudado# A tibble: 405 × 13
farm region zone district lon lat altitude cultivar shade
<dbl> <chr> <chr> <chr> <dbl> <dbl> <dbl> <chr> <chr>
1 1 SNNPR Bench Maji Debub Bench 35.4 6.90 1100 Local Sun
2 2 SNNPR Bench Maji Debub Bench 35.4 6.90 1342 Mixture Mid shade
3 3 SNNPR Bench Maji Debub Bench 35.4 6.90 1434 Mixture Mid shade
4 4 SNNPR Bench Maji Debub Bench 35.4 6.90 1100 Local Sun
5 5 SNNPR Bench Maji Debub Bench 35.4 6.90 1400 Local Sun
6 6 SNNPR Bench Maji Debub Bench 35.4 6.90 1342 Mixture Mid shade
7 7 SNNPR Bench Maji Debub Bench 35.4 6.90 1432 Mixture Mid shade
8 8 SNNPR Bench Maji Debub Bench 35.4 6.90 1100 Local Sun
9 9 SNNPR Bench Maji Debub Bench 35.4 6.89 1400 Local Sun
10 10 SNNPR Bench Maji Debub Bench 35.4 6.88 1342 Mixture Mid shade
# ℹ 395 more rows
# ℹ 4 more variables: cropping_system <chr>, farm_management <chr>, inc <dbl>,
# sev2 <dbl>